ByteDance تطلق SeedFold: نموذج متقدم لتوقع هياكل البروتين
أعلنت ByteDance عن إطلاق SeedFold، نموذج مفتوح المصدر لتوقع هياكل البروتين، متفوقًا على Google AlphaFold3 في عدة مقاييس، مع قدرة كبيرة على التعامل مع بيانات ضخمة وتحقيق نتائج دقيقة في مهام حيوية متعددة.
تفاصيل الخبر
SeedFold يعتمد على هندسة AlphaFold3 مع تحسينات رئيسية للتوسيع وزيادة الأداء:
- يحتوي على 923 مليون معلمة وتدرب على 26.5 مليون عينة من خلال تقنيات التقطير الكبيرة.
- تم تطوير نسخة SeedFold-Linear بكفاءة أعلى باستخدام Linear Triangular Attention لتقليل التعقيد الحسابي من O(n³) إلى O(n²).
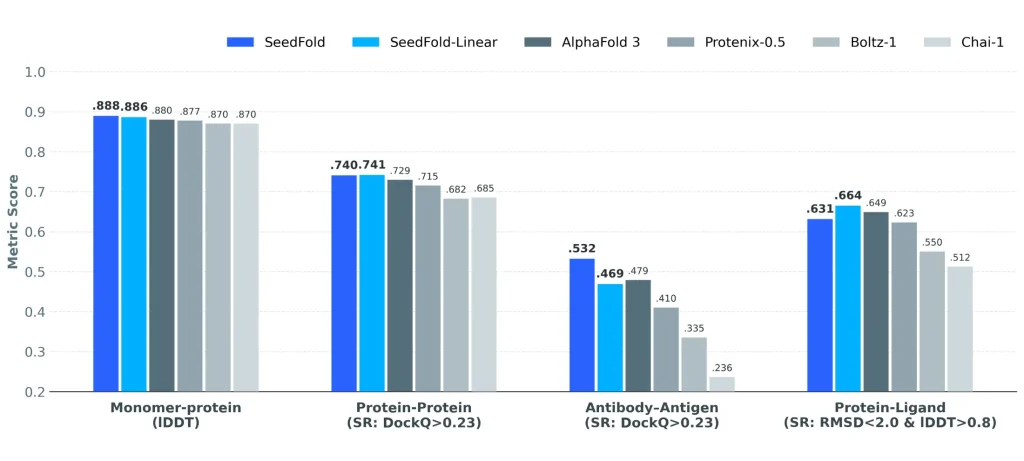
- النموذج نجح في اختبارات FoldBench، متفوقًا على AlphaFold3 في معظم مهام البروتين، بما في ذلك:
- البروتين-بروتين: 74.03% مقابل 72.93%
- Ab-Ag: +5.31% مقارنة بـ AlphaFold3
- Protein-Ligand: +1.58%
- Protein-RNA: +2.99%
- يعتمد النموذج على Pairformer لتحديث التمثيلات الزوجية، مع توسيع العرض من 128 إلى 512 لتعزيز قدرة النموذج على تشفير التفاعلات المعقدة.
- تقنيات Linear Triangular Attention تشمل نسخ Additive وGated لتقليل الذاكرة وزيادة كفاءة التدريب، مع تحسين الأداء في DNA وRNA.
الأهداف المستقبلية
تركز ByteDance على:
- تحسين قدرة التنبؤ بهياكل البروتين المعقدة لتسريع الأبحاث البيولوجية والدوائية.
- توسيع قاعدة البيانات التدريبية لدعم نماذج أكبر وأكثر دقة.
- تقديم أدوات مفتوحة المصدر للمجتمع العلمي لتسهيل الابتكار في تصميم البروتينات.
- استكشاف تقنيات هندسية جديدة لتوسيع النماذج دون التضحية بالجودة أو الكفاءة.
يمثل SeedFold خطوة جديدة نحو تعزيز التنبؤ الدقيق بهياكل البروتينات، مع قدرة مفتوحة المصدر تنافس AlphaFold3، ما يفتح آفاقًا واسعة للبحوث البيولوجية وتطوير الأدوية باستخدام الذكاء الاصطناعي.







